Products
特徴
- 130 万以上のアッセイが、Ensembl のヒト、マウス、ラットのmRNAおよびlncRNA 転写産物を最も幅広くカバー
- LNA プライマーによる卓越した感度と特異性
- 1 RNA コピーから始まる広いダイナミックレンジにわたる正確な検出
- 非特異的な増幅を徹底的に排除した最適設計
- QuantiNova SYBR® Green PCR 試薬により、わずか2時間で再現性のある結果
製品詳細
QuantiNova LNA PCR アッセイは、SYBR® Green ベースのqPCR 遺伝子発現分析による新しいスタンダードです。一般的な転写産物の検出から特定の転写産物のアイソフォームまで、ヒト、マウスおよびラットのmRNA またはlncRNA を正確かつ高感度に検出できるように、あらかじめデザインされた幅広いアッセイをご用意しました。LNA を組み込むことで、プライマーをより短くできるため、柔軟にターゲット上に設計ができるようになりました。 その結果、特定の転写産物の検出や近似したターゲットを区別して定量することができます。さらに、徹底したデザインの検証により、最適なパフォーマンスと優れた検出を保証します。またメジャーなmRNAやlncRNAのアッセイは、ウェットラボにて検証済みです。QuantiNova RT および SYBR® Green 試薬を使用して最適化されたシンプルなQuantiNova LNA PCR ワークフローは、わずか2時間で結果を手に入れられます。また室温でのセットアップが可能なため、自動化にも対応し、装置の運転終了を待つ作業計画の余裕も提供します。
製品の詳細については、弊社技術スタッフにお気軽に お問い合わせ ください。
パフォーマンス
LNAによるqPCRパフォーマンスの向上
QuantiNova LNA PCRアッセイは、厳しい設計基準とラボで検証されたアルゴリズムを適用しています。各厳密なアッセイ選択プロセスにより、信頼と正確な結果をゴールとした、特異的かつ増幅効率のよいプライマーセットが完成します。Tmの標準化とLNA による強化 により、プライマーは標準的なDNAプライマーよりも高い結合親和性が得られ、アッセイの感度と特異性が劇的に向上します。
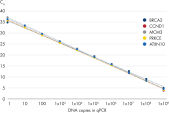
この感度の向上により、1 RNA分子までの優れた増幅効率が保証され、微量のサンプルからlncRNAなどの少量のターゲットをより簡単に検出できるようになります(図: QuantiNova LNA PCR Assays provide accurate, sensitive and linear quantification of targets over a wide dynamic range と QuantiNova LNA PCR Assays enable both high-expression and low-expression detection of mRNA 参照)。LNAの絶妙な配置で特異性の向上と高いS / N比を獲得し、1塩基のみ異なる配列の識別と、非特異的な増幅とプライマーダイマーの形成が排除されます。
LNA塩基の高い結合親和性により、転写物上でのプライマー配置の柔軟性が高まるため、設計の自由度が向上し、他の方法では難しいターゲットのアッセイを構築できます。 これにより、AUが豊富なターゲット、存在量の少ない転写産物、高い二次構造を持つターゲット、非常に複雑なサンプルであっても、ターゲットの識別と信頼性の高い定量が可能になります。
QuantiNova SYBR® Green PCR 試薬とのベストマッチ
QuantiNova LNA PCR アッセイは、QuantiNova SYBR® Green PCR 試薬と共に使用した場合に最適な結果と再現性を提供するように開発されました。1ステップqRT-PCRの場合はQuantiNova SYBR® Green RT-PCR キットが、また2ステップqRT-PCRには QuantiNova Reverse Transcription キットとQuantiNova SYBR® Green PCR キットが最適です。
QuantiNova のホットスタート機構により、GC含有量が高いテンプレートや複雑な二次構造などの難しいテンプレートでも、安心してqPCRを実施できます。また、lncRNA 解析にも最適です(図: Consistently high efficiencies throughout the expected GC content range of the human transcriptome 参照)。ホットスタートは、室温でのサンプル調製を可能にし、ロボットによる分注の自動化やサンプル調整後も余裕をもって装置にセットすることができます。 さらに、視覚的なピペッティングカラーインジケーターにより、目視による人為的なピペッティングエラーを防止します。
LNA設計のエキスパート
20年にわたるLNA 設計の経験により、50を超えるさまざまなパラメーターを組み込んだLNA 設計アルゴリズムを開発・最適化をしました。そして厳しい性能基準に対して徹底的にラボ検証がなされました。その結果、優れたターゲット検出をお約束するアッセイが完成しました。転写産物ごとに最大3つの異なるアッセイ設計を選択し、一般的なmRNA およびlncRNA に対するアッセイをすべてウェットラボで検証しました。あとはQuantiNova LNA PCR アッセイを混ぜるだけです。最適化に時間や費用はもう必要はありません。
迅速かつ簡便なワークフロー
迅速かつ簡単な2時間のワークフローは、時間と労力を節約し、自動化処理にも適しています。 シンプルなプロトコールは、いずれのqPCR装置とも互換性があります(図: QuantiNova LNA PCR Assays deliver consistent performance across all thermal cycler instruments 参照)。さらに、システム全体で使用できるため、研究ニーズに応じてアッセイからパネルへのシームレスな移行が可能になり、時間とサンプルを節約できます。
図参照
 QuantiNova LNA PCR Assays enable both high-expression and low-expression detection of mRNA.
QuantiNova LNA PCR Assays enable both high-expression and low-expression detection of mRNA.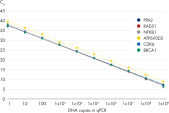 Consistently high efficiencies throughout the expected GC content range of the human transcriptome.
Consistently high efficiencies throughout the expected GC content range of the human transcriptome.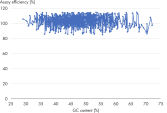 QuantiNova LNA PCR Assays deliver consistent performance across all thermal cycler instruments.
QuantiNova LNA PCR Assays deliver consistent performance across all thermal cycler instruments.
原理
ハイパフォーマンスなSYBR® Green による高いパフォーマンス
QuantiNova LNA PCR アッセイは、SYBR® Green による検出を行います。これは最適化された反応条件下において、優れた設計のプライマーを使用した場合、加水分解プローブ検出に比べていくつかの利点があります。まず、PCRの直後に融解曲線解析によりPCR の特異性を確認し、プライマーダイマーや非特異的PCR 産物の生成が確認できます。また、2本のプライマーと1本のプローブではなく、2本のプライマーしか必要としないため、アッセイ設計の柔軟性が向上します。プライマーは特異的なPCR増幅と検出色素のDNA結合特性により、ターゲット特異的な蛍光標識プローブが必要なく、アッセイのセットアップとランニングコストが削減されます。
包括的なカバレッジ
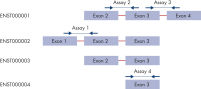
独自のアルゴリズムは130 万種以上のQuantiNova LNA PCR アッセイを設計し、感度、正確さに優れたmRNA およびlncRNA 解析を提供します。事前に設計されたアッセイは、Ensembl データベース内のヒト、マウス、ラットの遺伝子のほとんどの転写産物をカバーし、PCRベースの遺伝子発現研究を高いレベルで実現します。ほとんどのアッセイは、可能な限りイントロンをまたぎ、目的のRNAのみを検出するように設計されています。イントロンをまたがないアッセイは、ターゲットに1つのエクソンがある場合などになりますが、不要なシグナルはQuantiNova Reverse Transcription キットに含まれるgDNA 除去ステップにより容易に除去・低減できるように設計されています。
ターゲットに最適なアッセイの選択
事前に設計されたQuantiNova LNA PCRアッセイを使用すれば、ヒト、マウス、またはラットのmRNAまたはlncRNAを正確かつ高感度に検出できます。それは一般的な転写産物、特定の転写産物または転写産物アイソフォームを見分けた検出などを含みます。
ほとんどのヒト、マウス、ラットの遺伝子には転写産物が1つしかありませんが、複数の転写産物がある場合は、同じアルゴリズムを使用して転写産物ごとに最大3つのアッセイを設計しました。これらのアッセイのデザインとプライマーの配置は、使用する目的に合わせて異なります。弊社のアッセイ選択ガイドは、各カテゴリーから最適なアッセイをすばやく特定するのに役立ちます。ターゲットのアッセイを検索したら、結果を確認し、目的の用途に一致する推奨アッセイを確認してください。
- Best coverage:一般的な転写産物の検出
- Best transcript assay:特定の転写産物の検出
- Best transcript-specific assay:特定の転写産物アイソフォームの区別して検出
詳細については、下表を参照してください。
| 遺伝子をカバーするアッセイ | 転写産物特異的なアッセイ | ||
|---|---|---|---|
| QIAGEN 推奨のアッセイ | “Best coverage” 表記のアッセイ | “Best transcript assay” 表記のアッセイ | “Best transcript-specific assay” 表記のアッセイ |
| アッセイデザインとカバレッジ | 対象遺伝子の生物学的に関連した転写産物の多くをカバー | 対象の遺伝子転写産物を特異的に検出するように最適化され、転写産物の多くのアイソフォームをカバー | 転写産物のスプライスバリアントに特異的 |
| 使用用途 | 一般的な転写産物のスクリーニングや目的の遺伝子がサンプル中で発現しているかどうかを検出するときできるだけ多くの転写産物やアイソフォームの検出をするとき | 特異的転写産物を検出するとき | 転写産物の特異的アイソフォーム間を区別するとき |
無料のデータ解析ツール
GeneGlobe データ解析センター の無料のWeb ベースのデータ解析ツールは、使いやすいウィザードが含まれており、データの標準化と解析を指示に従って選択するだけで、論文や学会発表に対応した結果の図を作成できます。
あらゆる研究のためのリファレンス遺伝子アッセイ
ヒト、マウス、ラットの幅広いリファレンス遺伝子アッセイは、高品質なデータの標準化と、信頼ある結果担保するために利用できます。 これらのアッセイは、内因性のコーディングRNA、ロングノンコーディングRNA(lncRNA)、および一般に多種多様な組織で恒常的に発現される小さな核小体RNAをターゲットとしています。 リファレンス遺伝子のアッセイは蛍光色素FAMで標識されていて、QuantiNova LNA PCRシステムのリファレンス遺伝子として検証され、QuantiNova RTおよびPCR試薬により適切に機能します。
mRNA / lncRNA qPCR 結果の標準化
標準化により、実験における生物学的に変化に関係のない、技術的およびサンプル間での誤差を取り除くことができます。適切な標準化は、リアルタイムPCR の実験結果を正しく解析および解釈するために重要です。一般的には、安定して発現するリファレンス遺伝子が標準化に用いられます。
実際のmRNA / lncRNA 発現解析をする前に、いくつかの内因性のコントロールリファレンス遺伝子を検証することをおすすめします。これらの候補遺伝子は、一連の実験においてすべてのサンプルで安定して発現していると思われる遺伝子から選択する必要があります。それら安定して発現しているmRNA またはlncRNAは、文献や既存データ(例えば、NGS またはqPCR パネルスクリーニング)などでも示されています。QuantiNova LNA PCR システムでは、安定発現する傾向にある候補遺伝子を検証済みリファレンス遺伝子アッセイを提供しています。
すべてのリファレンス遺伝子候補は、各実験系で経験的に検証する必要があります。多くのmRNA / lncRNA をプロファイリングするときのPCR パネルを標準化する1つの選択肢として、グローバル平均、つまり、すべての発現したmRNA / lncRNA の平均に対して標準化することです。これは、高いコールレート(発現した遺伝子)のサンプルでは良い選択肢ですが、コールレートの低いサンプルでは注意して使用する必要があります。また、一般的な遺伝子発現レベルが変化するサンプルでは、これは適切な選択肢ではありません。標準化の詳細なガイダンスは、GeneGlobe データ解析センターでも記載があります。
操作手順
1ステップまたは2ステップqRT-PCR の選択
各QuantiNova LNA PCR アッセイは、特定の遺伝子に対するフォワードおよびリバースプライマーを混合した凍結乾燥品として提供されます。TE(pH 8.0)でプライマーを再溶解するだけで、簡単に10xプライマー溶液を調製できます。
QuantiNova LNA PCR アッセイは、定評のあるQuantiNova ケミストリーを使用して最適化されています。QuantiNova Reverse Transcriptionキットで逆転写を行うと、最良の結果が得られ、そのcDNA は、QuantiNova SYBR® Green PCR Kit のマスターミックスと、選択したQuantiNova LNA PCR アッセイを組み合わせてqPCR によって定量解析を行います。
1ステップqRT-PCRの場合は、反応条件をさらに最適化する必要がないQuantiNova SYBR® Green RT-PCR キットがおすすめです。プライマー、RNA テンプレート、RT-MixをSYBR® Green RT-PCR マスターミックスに添加するだけで、反応を始められます。
出荷と配送
QuantiNova LNA PCR アッセイは、室温で出荷されます。在庫にあるアッセイならば数日のうちにお届けしますが、初めてのご注文の製品は、お届けまでお時間を頂戴することが予想されます。
QuantiNova LNA PCR システムを始めるのに必要なもの
Reverse transcription: QuantiNova Reverse Transcription キット
qPCR mastermix: QuantiNova SYBR® Green PCR キット
One-Step qRT-PCR (optional): QuantiNova SYBR® Green RT-PCR キット
アッセイまたはパネル
- QuantiNova LNA PCR Assays
- QuantiNova LNA PCR Reference Assays
- QuantiNova LNA PCR Custom Assays
- QuantiNova LNA PCR Focus Panels
- QuantiNova LNA PCR lncRNA Focus Panels
- QuantiNova LNA PCR Custom Panels
- QuantiNova LNA PCR Flexible Panels
アプリケーション
QuantiNova LNA PCR アッセイは、次のようなアプリケーションに非常に適しています:
- mRNA およびlncRNA 発現分析、プロファイリングおよび定量化
- RNA-seq 遺伝子発現データの検証
- 遺伝子発現プロファイリング
- シグナルとパスウェイの解析
- LNA GapmeR またはsiRNA による遺伝子発現ノックダウンの確認
- 疾患関連のバイオマーカーのスクリーニング、同定、検証を含むバイオマーカーの開発
- 遺伝子発現に関連する表現型の変化のモニタリング
裏付けデータと数値
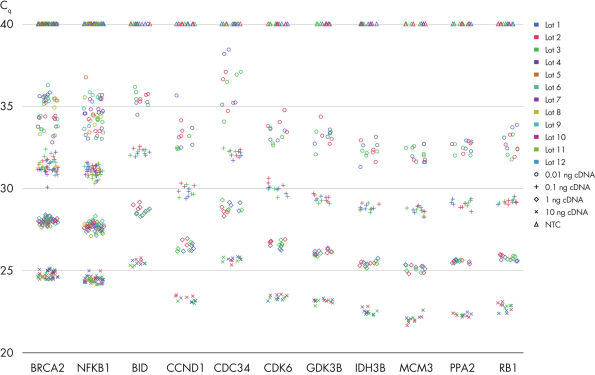
Demonstrated lot-to-lot reproducibility.